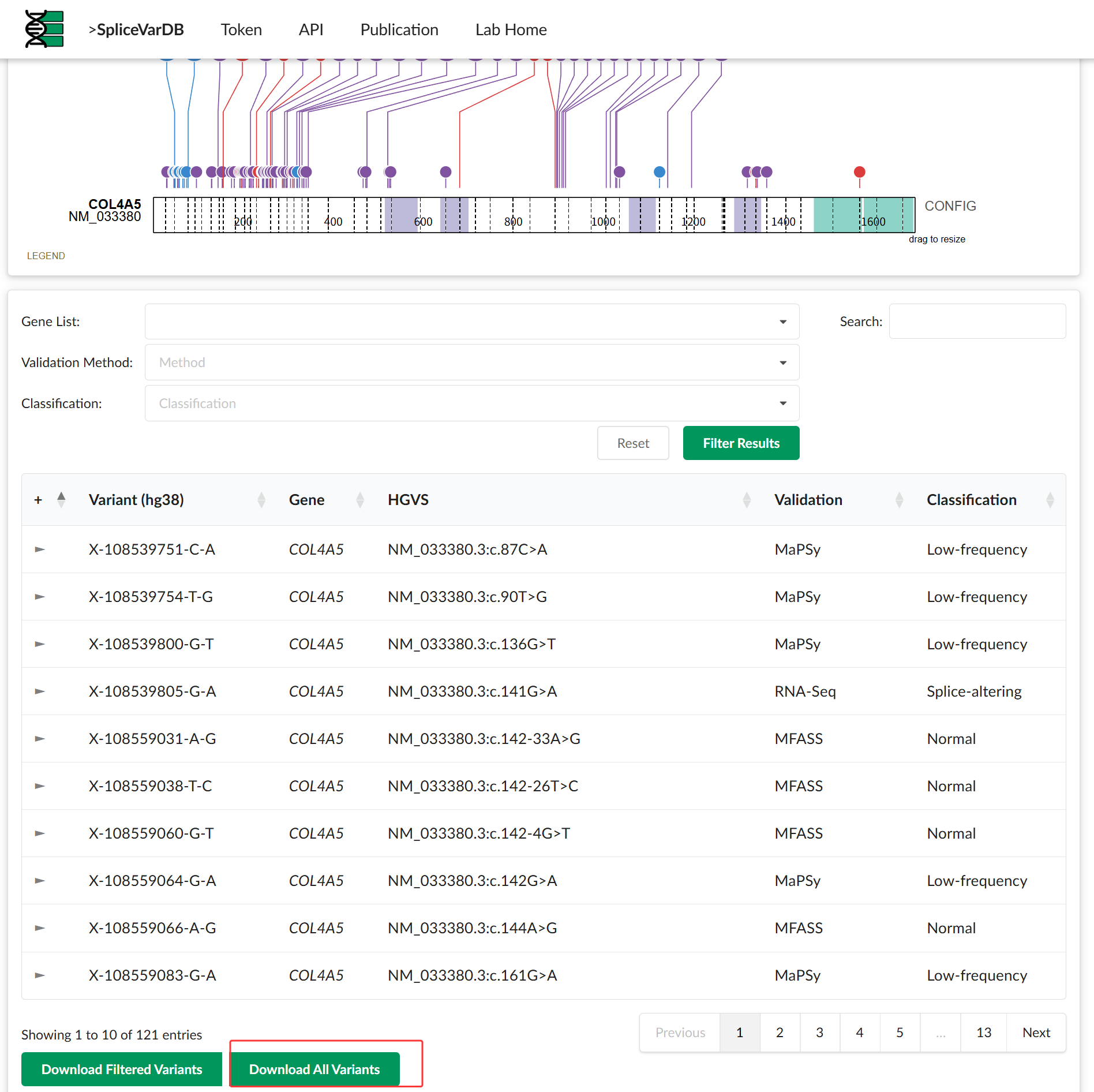
这个网址 SpliceVarDB 不是 ClinVar 那种通用临床变异总库,而是一个更聚焦的数据库:专门收录"经过实验验证会影响剪接(splice-altering)的变异" 。主页上直接写了,用户可以提交已发表、预印本或未发表但有支持证据的、经实验验证的剪接改变变异 ,并在人工审核后纳入数据库。(SpliceVarDB)
你可以把它理解成:
-
ClinVar:更广义的临床变异数据库,关注致病性、临床解释、疾病关联等
-
SpliceVarDB :更专门,重点是哪些变异真的会改变 RNA 剪接 ,而且强调实验验证过
下载以后的文件有下面几列:
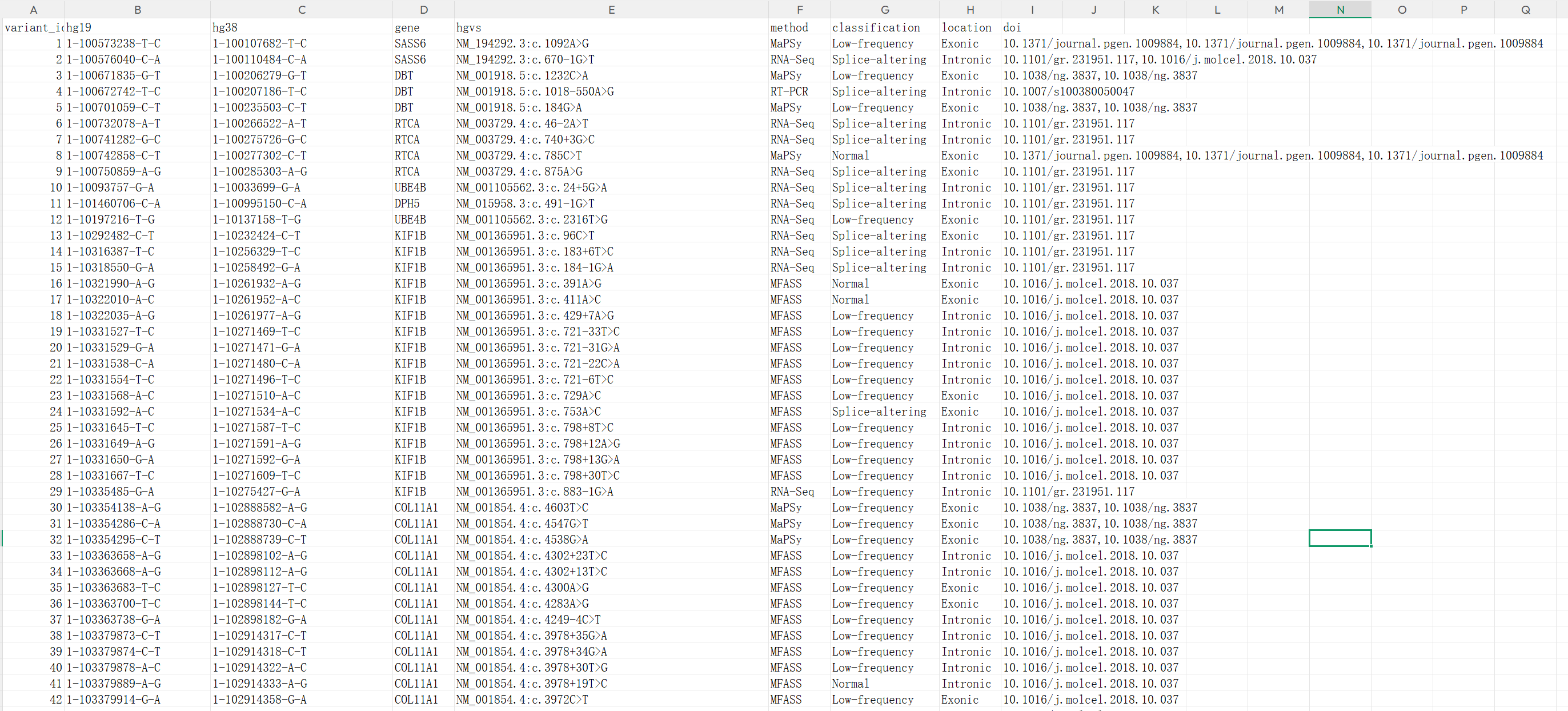
variant_hg19
这是变异在 hg19 / GRCh37 参考基因组坐标下的表示。
例如 1-100573238-T-C 的意思就是:
1 号染色体、坐标 100573238、参考等位基因 T、变异后是 C。
一般格式就是:
染色体-位置-REF-ALT
hg38
这是同一个变异在 hg38 / GRCh38 参考基因组坐标下的表示。
所以 variant_hg19 和 hg38 是同一条变异在两个不同参考基因组版本中的坐标。SpliceVarDB 网站本身也支持在 hg38 和 hg19 两个版本之间切换。
gene
这个变异对应的基因符号,比如 SASS6、DBT、RTCA、KIF1B。
也就是这个变异被认为影响哪个基因的剪接。
hgvs
这是用 HGVS 命名法 写的标准变异描述。
例如:
-
NM_194292.3:c.1092A>G -
NM_001918.5:c.1232C>A
这里通常可以拆成:
-
NM_...:转录本 accession -
c.:表示在 coding DNA/transcript 坐标上的描述 -
1092A>G:第 1092 个 cDNA 位点,A 变成 G
如果像 c.670-1G>T、c.1018-550A>G 这种带 -1、-550 的,说明这个位置在外显子边界附近或更深的内含子区域,是相对外显子坐标来写的。
method
这是这个变异的实验验证方法 ,也就是 SpliceVarDB 里的 Validation / Validation Method 。网页上也把这一列叫作 Validation。(SpliceVarDB)
你截图里常见的几种:
-
RNA-Seq:用 RNA 测序数据观察这个变异是否改变剪接产物
-
RT-PCR:用逆转录 PCR 检测异常剪接转录本
-
MFASS:一种大规模剪接功能实验体系
-
MaPSy:也是一种用于评估变异对剪接影响的高通量实验方法
所以 method 说的不是"预测模型",而是这个标签是靠什么实验手段得到的。SpliceVarDB 的说明里也明确说,它整合的是来自多种实验协议的验证数据。
classification
这是这个变异在 SpliceVarDB 里的剪接效应分类。数据库把变异按支持证据强弱分成几类,核心包括:
-
splice-altering:有比较明确证据表明它会改变剪接
-
normal:有比较强证据表明它不改变剪接,可当作高质量负例
-
low-frequency splice-altering / low-frequency:介于两者之间,证据较弱、效应较小、或结果不够"纯粹"
-
某些情况下还会有 conflicting:不同实验结果互相冲突
location
这是这个变异在基因结构里的大致位置类型,比如:
-
Exonic:在外显子里
-
Intronic:在内含子里
SpliceVarDB 说明里提到,它的 splice region/location 是按离最近 canonical exon 的距离来计算的,也包含 UTR 区域。