01
导语
各位同学,大家好。做影像组学最怕什么?模型AUC刷得飞起,但一问"为什么这个特征能预测疗效",当场哑火 ------这就像算命先生掐指一算挺准,但你要问他凭什么,他只能说"天机不可泄露"。真正能发高分、经得起推敲的研究,早就不是单纯比谁AUC高了,而是想方设法给影像特征找个"生物学娘家" ,让MRI上的明暗变化,能跟细胞、通路、免疫微环境对上话。今天咱们通过这篇MR‑DELTAnet文献,看看人家是怎么用纵向MRI预测病理完全缓解,再靠单细胞测序把"高分/低分"背后的免疫故事讲圆 的。看完你就明白:影像组学挂靠机制,不是硬凑,而是有套路、有逻辑、能复制的。

**★题目:**MR-DELTAnet: A Longitudinal MRI-Transformer Model Predicting Pathological Complete Response and Revealing Immune Microenvironment via scRNA-seq in Locally Advanced Rectal Cancer
(MR-DELTAnet:一种纵向MRI-Transformer模型,通过单细胞RNA测序预测局部晚期直肠癌的病理完全缓解并揭示免疫微环境)
★期刊:《Advanced Science》(中科院1区,IF=14.1)
**★研究疾病:**局部晚期直肠癌(LARC)
**★生物学机制:**肿瘤免疫微环境(TME)的异质性
**★发表时间:**2025年12月
02
研究背景-从 "临床问题" 落到 "生物学问题"
局部晚期直肠癌(LARC)的标准治疗策略是新辅助放化疗(NCRT)后行全直肠系膜切除术,其中约30%的患者可获得病理完全缓解(pCR) 。这部分患者若能术前准确识别,有望接受器官保留或等待观察策略,避免根治性手术带来的功能损害,尤其对于低位直肠癌、老年或需保留生育功能的患者具有重要临床意义。然而,目前临床常用的磁共振肿瘤退缩分级(mrTRG) 在预测pCR方面存在敏感性和阳性预测值不足 的突出问题,其主要原因在于NCRT后肿瘤区域常出现纤维化重塑和治疗相关炎性浸润,与残留活肿瘤在影像上难以区分。尽管深度学习已在肿瘤影像分析中展现出强大能力,但既往研究多聚焦于单一时间点的静态影像 ,无法捕捉治疗过程中肿瘤的动态病理生理演变 。更关键的是,现有模型普遍缺乏生物学可解释性 ,其预测结果难以转化为临床对肿瘤微环境(TME)状态的深入理解。因此,研究问题从"如何提高pCR预测准确性"进一步下沉到生物学问题 :pCR与非pCR患者在肿瘤免疫微环境 上究竟存在何种本质差异?这种差异是否可通过纵向影像特征 进行非侵入性表征?具体而言,pCR患者是否呈现出细胞毒性T细胞主导的免疫激活状态 ,而非pCR患者是否具有髓系细胞富集、代谢重编程及免疫抑制特征?这一生物学问题的解答,将为影像模型赋予真正的机制内涵。
03
研究目的(明确写出"三层目的")
本研究设定了三个层次 的研究目的。第一层:模型开发目的 。构建一个基于纵向MRI 的Transformer深度学习框架------MR-DELTAnet,通过整合治疗前后的T2加权影像,并引入Delta高效潜在时间注意力机制 ,实现对LARC患者NCRT后pCR的术前精准预测,以填补临床非侵入性评估工具的空白。第二层:临床验证目的 。在多中心回顾性队列 (共1026例)中系统评估该模型的预测性能,包括训练集、内部验证集和外部验证集的ROC曲线、校准曲线等指标;进一步分析模型预测评分与患者无病生存期(DFS)和总生存期(OS) 的关联,并在多因素Cox回归中验证其作为独立预后因子的价值;同时探索预测评分与临床病理特征(如CEA水平、肿瘤距肛缘距离等)的分布关系,以明确模型的临床相关性和预后分层能力。第三层:机制解释目的 。通过独立单细胞RNA测序队列(26例,137,666个细胞) ,揭示MR-DELTAnet预测评分背后的免疫微环境差异 ,具体包括:高评分与低评分患者在免疫细胞组成(T细胞、髓系细胞)、功能通路活性(氧化磷酸化、免疫激活)、巨噬细胞极化状态(M1/M2)、调节性T细胞(Treg)与CD8+ T细胞间通讯等方面的生物学异质性,从而实现从影像表型到分子机制的跨尺度解释,增强模型的临床可信度与生物学有效性。
04
研究思路(最核心:怎么挂靠机制)
本研究的核心思路是以模型预测作为分层锚点,反向揭示影像表型背后的生物学机制 ,而非直接训练影像预测基因表达。具体分为四个步骤。第一步:纵向影像模型构建 。收集LARC患者NCRT前后的T2加权MRI图像,采用Transformer架构,设计交叉注意力机制 对齐治疗前后影像特征,引入Delta模块 量化多尺度特征差异,最终输出pCR预测概率(0-1评分)。通过多中心数据训练与验证,确保模型具有稳定的判别性能(AUC达0.88-0.93)。第二步:临床与预后关联 。将模型预测评分与患者生存数据、临床病理参数进行关联分析,验证高分(预测非pCR)与低分(预测pCR)患者在DFS和OS上的显著差异 ,并确认模型评分是独立预后因素。第三步:基于预测评分进行生物学分层 。在独立scRNA-seq队列中,同样应用MR-DELTAnet获得每位患者的预测评分,以0.5为阈值将患者分为高评分组与低评分组 。这一设计的关键在于:模型输出不再仅仅是预测标签,而是作为划分不同免疫微环境状态的工具 。第四步:单细胞层面机制验证 。对手术标本进行scRNA-seq,通过UMAP聚类、Ro/e富集分析、GSEA、细胞通讯分析等方法,系统比较两组患者在免疫细胞亚群比例、功能通路活性、巨噬细胞极化倾向、Treg与CD8+ T细胞互作模式 等方面的差异。最终建立起纵向影像特征→pCR预测评分→特定免疫细胞状态(髓系富集/氧化磷酸化↑ vs CD8+ T富集/细胞毒性↑) 的因果解释链条,实现了影像组学与生物学机制的深度挂靠。
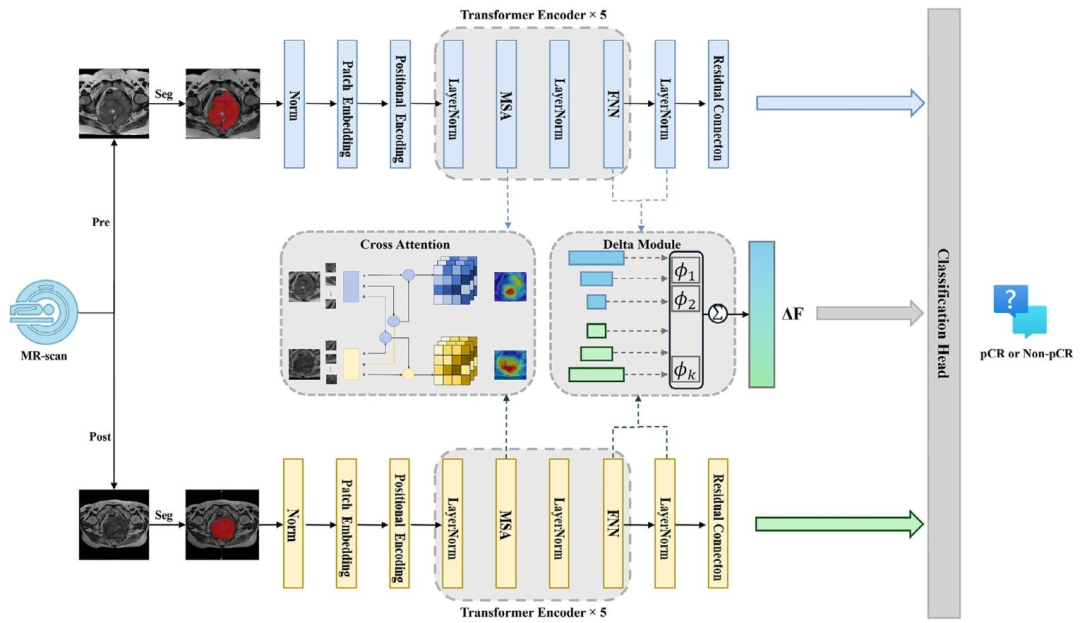
图 6(模型架构图) :详细展示了MR-DELTAnet的内部结构,包括交叉注意力机制 对齐治疗前后影像特征、Delta模块 量化多尺度时序差异、以及分类决策模块。该架构的创新在于高效捕捉治疗诱导的动态变化,从而提取与肿瘤微环境演变相关的影像生物标志物。
05
数据和方法(机制部分怎么设计)
数据 :研究共纳入来自四个中心的1026例局部晚期直肠癌患者 ,其中中心A的845例按0.75:0.25随机划分为训练集(633例) 和内部验证集(212例) ,来自中心B、C、D的181例 作为外部验证集 ,用于模型开发与pCR预测性能评估;另外纳入841例具有随访数据的患者 用于生存预后分析(DFS/OS);同时,独立收集26例患者的手术标本 进行单细胞RNA测序(137,666个细胞),作为机制验证队列,用于揭示模型预测评分背后的免疫微环境差异。
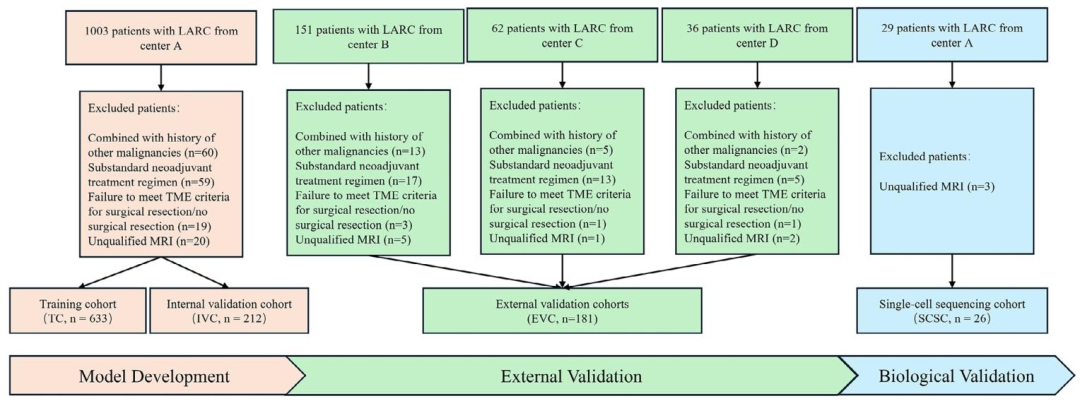
图 2:患者筛选流程图
方法 :影像采集与预处理 → 收集治疗前后T2加权MRI,手动勾画肿瘤感兴趣区域(ROI) → 模型构建(MR‑DELTAnet) → 采用Transformer架构,通过交叉注意力机制 对齐治疗前后影像特征,Delta模块 量化多尺度特征差异,分类决策模块 输出pCR预测概率 → 训练策略 → 动态数据增强、平衡批次采样、自适应损失函数(Class‑Balanced Focal Loss + 跨时间对比正则化),AdamW优化,基于F1分数的早停 → 性能评估 → 绘制ROC曲线,计算AUC、灵敏度、特异度,使用校准曲线评估预测概率与实际pCR的一致性 → 可解释性分析 → 采用Guided Grad‑CAM 可视化关键激活区域 → 生存分析 → Kaplan‑Meier曲线及Cox回归评估预测评分与DFS/OS的关联 → 单细胞机制验证 → 将模型预测评分(阈值0.5)将26例患者分为高/低分组,对手术标本进行scRNA‑seq,经UMAP降维聚类 鉴定主要细胞类型及T细胞/髓系细胞亚群,采用Ro/e富集分析 比较组间细胞丰度,GSEA 及GO 分析通路活性,CellChat解析细胞间通讯网络,从而建立影像预测评分与免疫微环境表型(髓系富集/氧化磷酸化↑ vs CD8+ T富集/细胞毒性↑)之间的生物学关联。
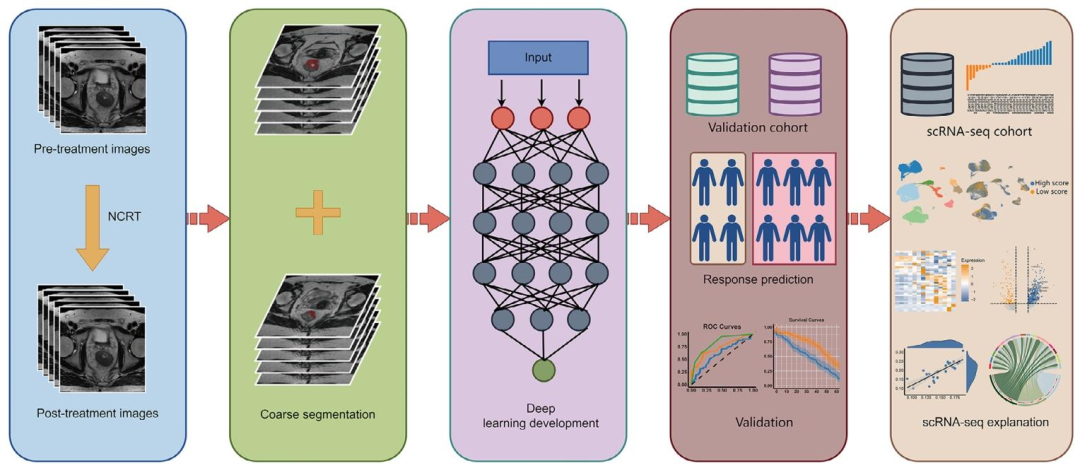
图 1:研究整体工作流程图
06
研究结果("从表型到机制")
①表型层面(模型性能) :MR-DELTAnet在训练集中AUC达0.93(95% CI: 0.90-0.96) ,内部验证集为0.88(95% CI: 0.82-0.94),外部验证集为0.90(95% CI: 0.79-1.00),显示出稳定的跨中心泛化能力 。消融研究证实各模块均贡献显著。多因素分析显示,模型预测评分是独立预后因子 。根据预测评分(阈值0.5)将患者分为高/低分组,Kaplan‑Meier分析表明,低评分患者的无病生存期和总生存期均显著优于高评分患者 (log‑rank P<0.05),而实际pCR组仅在DFS上有优势。Guided Grad‑CAM显示,pCR组治疗前后激活区域均集中于肿瘤核心,非pCR组则从核心向外周弥散并缩小,提示周边侵袭性生长模式。
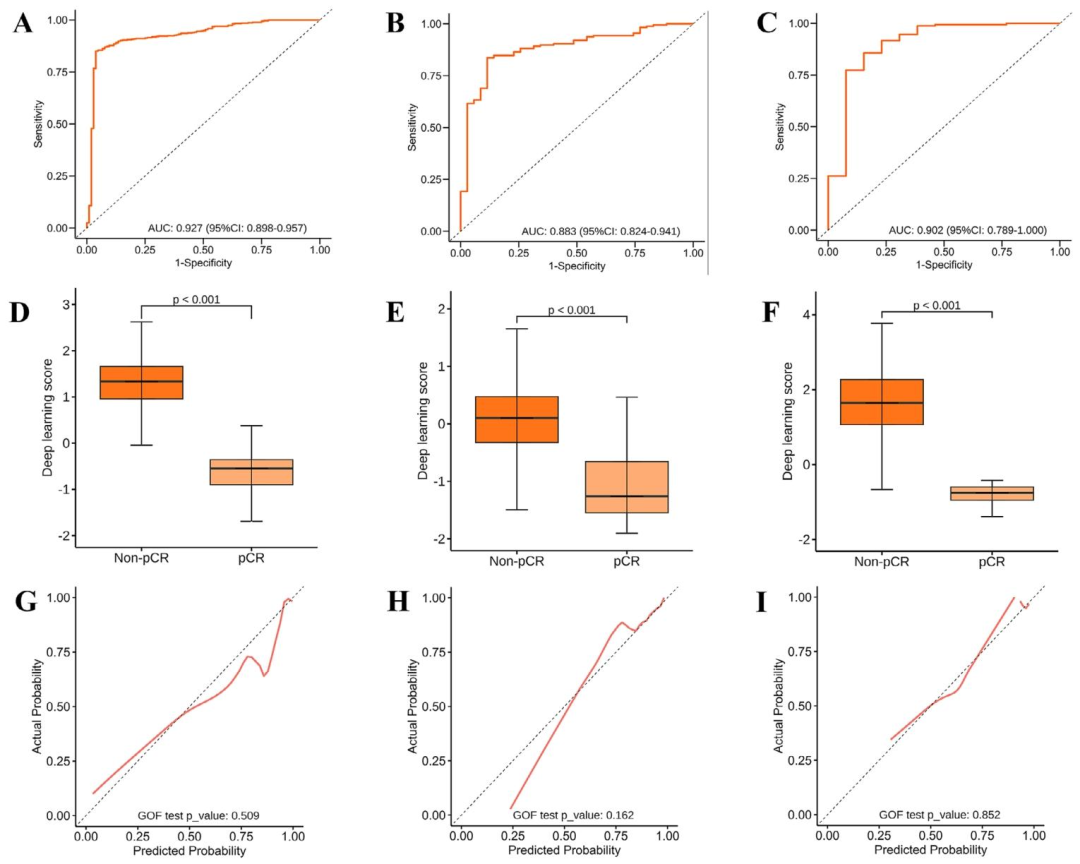
图3(模型性能评估) :通过ROC曲线展示MR-DELTAnet在训练集(AUC=0.93)、内部验证集(0.88)和外部验证集(0.90)的稳定判别能力 ;箱线图显示pCR与非pCR组的深度学习评分分布差异显著;校准曲线表明预测概率与实际观察结果高度一致。这一表型层面的高性能为后续将预测评分作为生物学分层工具奠定了前提条件。
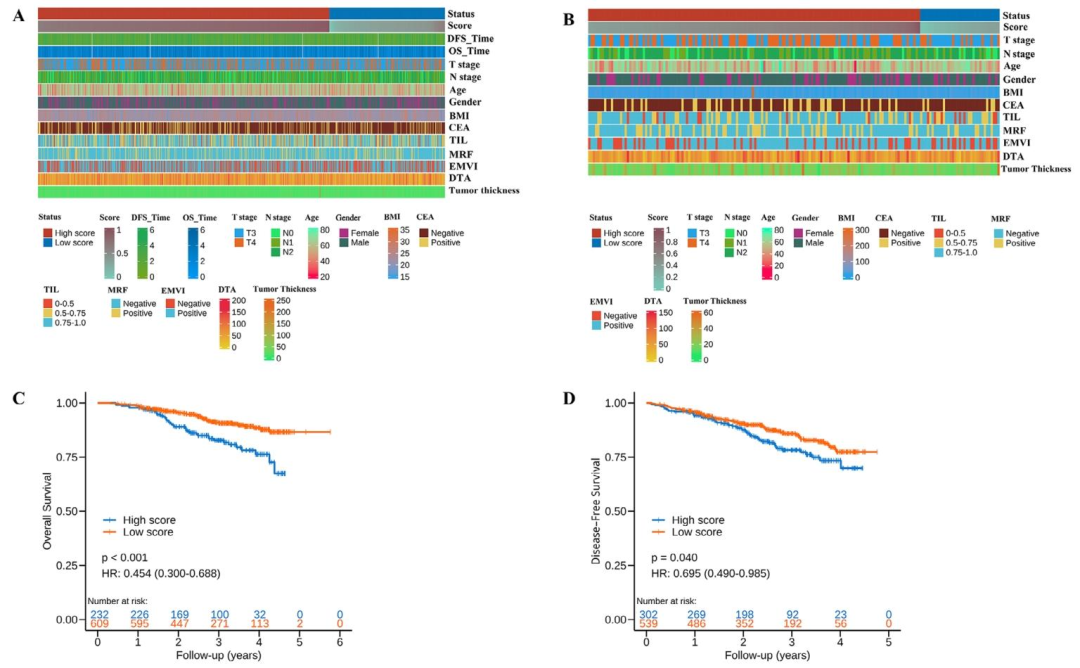
图 4(临床特征与生存分析) :热图对比了高低评分组在临床病理变量上的分布,发现低评分组距肛缘距离更大、CEA阳性率更低;Kaplan-Meier曲线显示低评分患者的无病生存期和总生存期均显著优于高评分患者 。该图将影像预测评分与真实临床结局直接挂钩,说明模型评分不仅是统计指标,更是具有预后价值的生物标志物,为机制解释提供了临床必要性。
②机制层面(scRNA-seq) :对26例患者(137,666个细胞)的单细胞测序发现,高评分(预测非pCR)组呈现髓系细胞富集 ,尤其是Macro_SPP1巨噬细胞,其氧化磷酸化通路显著上调 ,M2极化评分升高,提示免疫抑制表型 。低评分(预测pCR)组则表现为CD8+ T细胞富集 ,其中CD8_Tc_GZMB亚群比例增高,细胞毒性评分 显著增强。GO分析显示低评分组富集免疫激活及NF-κB通路 。细胞通讯分析进一步揭示,高评分组中CD4_Treg_FOXP3细胞向CD8+ T细胞发出更强的抑制信号 ,证实模型评分能够有效区分免疫抑制与免疫激活两种截然不同的微环境状态。
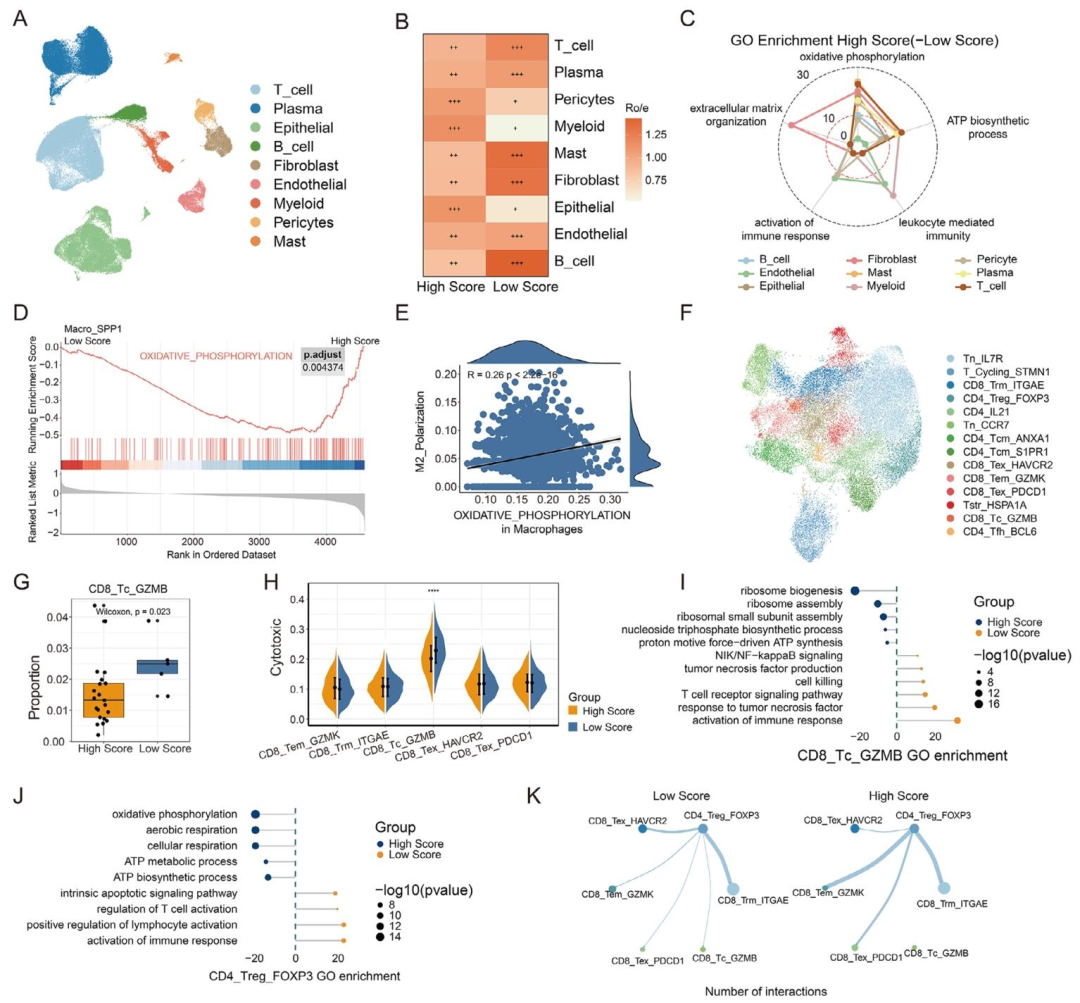
图 5(单细胞免疫微环境) :这是影像组学挂靠生物学机制的核心图 。UMAP显示九大细胞类型;Ro/e分析表明高评分组髓系细胞富集 、低评分组T细胞富集 ;GSEA揭示高评分组Macro_SPP1巨噬细胞氧化磷酸化通路上调、M2极化增强;T细胞分析显示低评分组CD8_Tc_GZMB比例高、细胞毒性评分高;细胞通讯图显示高评分组Treg向CD8+ T细胞发送更强抑制信号。这些结果将影像预测评分直接映射为免疫抑制vs免疫激活的微环境状态。
07
讨论(把机制故事讲圆)
本研究成功开发了MR‑DELTAnet,一个基于纵向MRI的Transformer模型 ,能够术前精准预测局部晚期直肠癌患者新辅助放化疗后的病理完全缓解,在多中心验证中AUC达0.88‑0.93,显著优于传统静态影像方法 。与既往仅追求预测准确性的深度学习研究不同,本研究通过独立单细胞RNA测序队列 将模型预测评分与肿瘤免疫微环境进行直接关联,构建了**"影像表型→预测评分→生物学机制"** 的完整解释链条。研究发现,高评分(预测非pCR)患者呈现髓系细胞富集、氧化磷酸化通路上调、M2型巨噬细胞极化及Treg介导的CD8+ T细胞抑制 ,形成免疫抑制微环境;而低评分(预测pCR)患者则以CD8+ 细胞毒性T细胞主导、免疫激活通路富集 为特征。这一发现不仅解释了为何部分患者对治疗抵抗,也为影像模型提供了细胞层面的生物学验证 ,极大增强了临床医生对"黑箱"模型的信任。值得注意的是,模型在生存预后分层上优于传统病理退缩分级,提示纵向影像动态变化比静态残瘤负荷更能反映肿瘤的时空演化特性 。尽管存在回顾性设计、手动勾画ROI、仅使用T2序列等局限,但该研究开创了影像组学与单细胞转录组学深度融合 的范式,为未来精准肿瘤学中非侵入性免疫微环境评估提供了可推广的框架。
08
这篇文献的可借鉴思路
该文献为影像组学/深度学习研究者提供了多条可直接迁移的范式 。第一,从静态影像转向纵向建模 :治疗前后的变化信息远比单时间点丰富,设计Delta模块或差分注意力机制可成为通用策略。第二,模型不直接预测基因,而是作为分层工具 :先输出预测评分,再依据评分划分亚组,最后在分子层面验证组间差异------这是低成本、高可信的机制挂靠路径 ,尤其适用于难以获取大样本多组学数据的场景。第三,选择可验证的"聚焦通路" :不泛泛谈免疫微环境,而是落到氧化磷酸化、M2极化、Treg‑CD8互作 等具体、可操作的通路,增强机制故事的可信度。第四,单细胞验证的设计时机 :可在模型开发后,针对少量代表性样本进行深度的单细胞测序,不必在训练阶段就整合多组学,从而降低数据获取门槛 。第五,可视化叙事的层次 :图5从UMAP全局分群 → Ro/e富集 → GSEA通路 → 细胞通讯,逐层递进,可复制到其他肿瘤类型的影像‑免疫研究中。第六,临床转化导向 :始终围绕"哪些患者可免于手术"这一真实痛点,使机制研究服务于临床决策,而非为发文而做机制。这些思路可广泛应用于直肠癌以外的乳腺癌、食管癌、肺癌等接受新辅助治疗的实体瘤研究。
09
结语
总而言之,影像组学研究的升级之路,就是从"算分"走向"讲理" 。这篇文献给我们的最大启发是:模型预测结果不是终点,而是分层探索生物学机制的起点 。用预测评分划分患者,再用单细胞测序去验证组间差异,既不烧钱堆数据,又能把宏观影像和微观免疫状态牢牢绑定 。以后你做研究,也别忘了多问一句:我的影像特征,到底在反映肿瘤微环境里的什么故事? 只有把这个问题回答清楚了,你的模型才算真正站住了脚。愿大家都能从"黑箱操作工"升级为"疾病故事讲述者",写出有深度、有机制、有灵魂的好文章!
参考文献:Cao W, Chen H, Li J, Zheng Y, Xie L, Xiao G, Wang Z, Yuan F, Chen J, Sun C, Dai J, Zeng J, Wang X, Wu L, Lin H. MR-DELTAnet: A Longitudinal MRI-Transformer Model Predicting Pathological Complete Response and Revealing Immune Microenvironment via scRNA-seq in Locally Advanced Rectal Cancer. Adv Sci (Weinh). 2026 Feb;13(11):e17721. doi: 10.1002/advs.202517721. Epub 2025 Dec 19. PMID: 41417633; PMCID: PMC12931229.