文章目录
介绍
核心问题与研究背景
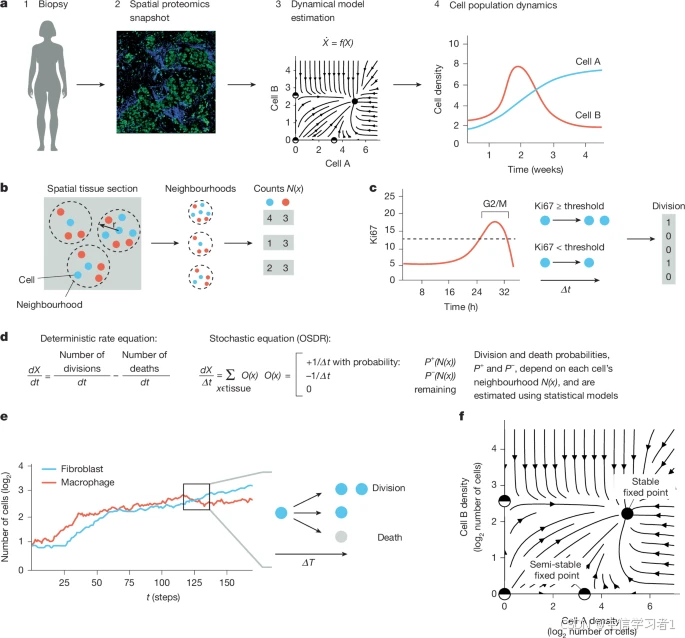
生理和病理过程(如炎症和癌症)是由细胞间相互作用随时间演化而产生的。然而,由于组织活检只能提供单一时间点的"快照",传统方法难以追踪人体组织内细胞群体随时间的变化动态
。
主要方法:OSDR
研究团队提出了一种名为 OSDR(One-Shot tissue Dynamics Reconstruction,一次性组织动态重建) 的新方法
:
- 核心思想:利用空间组学(spatial omics)快照,基于细胞分裂标记物(如Ki67),估计细胞的分裂和清除速率如何受周围细胞组成(neighborhood composition)的影响
- 技术基础:使用成像质谱流式细胞术(IMC)等空间蛋白质组学技术,分析约500μm × 500μm的组织切片
- 建模方式:将细胞邻域组成映射到状态空间,构建相图(phase portrait)展示细胞群体变化的方向和幅度,识别稳定点和不稳定点
主要发现
1. 成纤维细胞-巨噬细胞回路
通过分析715例乳腺癌患者的空间蛋白质组学数据,OSDR重建了成纤维细胞与巨噬细胞的相互作用回路,发现两个稳态固定点,分别对应"热纤维化"和"冷纤维化"状态,这与直接测量动力学的共培养实验结果一致
。
2. T细胞和B细胞的脉冲生成回路
OSDR发现肿瘤微环境中存在T细胞和B细胞组成的可兴奋回路(excitable circuit):
- 当CD4 T细胞密度超过阈值时,会触发免疫脉冲
- T细胞先上升,随后B细胞抑制T细胞,两者共同下降
- 脉冲后存在不应期(refractory period),在此期间B细胞仍高表达而T细胞低,新的脉冲无法产生
- 这提示癌症免疫监视是以**时间性爆发(temporal flares)**形式运作,而非文献中隐含的稳态图景
3. 预测治疗反应
研究应用OSDR分析三阴性乳腺癌临床试验的纵向活检样本:
- 基于治疗开始时的活检样本,OSDR能预测肿瘤细胞群体在治疗反应者中会崩溃,而在无反应者中不会
- 这种预测能力不依赖于初始组织状态或平均增殖率,而是源于细胞间相互作用随时间的演化
方法验证
- 通过模拟数据验证:仅需数千个细胞即可可靠重建固定点和吸引域
- 结果对重采样、死亡率假设、邻域大小等参数具有稳健性
意义与应用前景
OSDR为从患者活检的空间快照推断细胞群体动态提供了通用框架,可应用于广泛的空间蛋白质组学或转录组学检测,为理解组织动态和预测治疗反应开辟了新途径
类比
OSDR ≈ 从一张"班级合影"推断整个学期的动态
传统困境
想象你是一位老师,想知道班级里"学霸"和"活跃分子"是怎么互相影响的。但你只有一张期末合影,没有整个学期的监控录像。怎么办?
OSDR的巧妙思路
第一步:看"表情"猜状态(Ki67标记)
合影里,有些学生面带疲惫(刚考完试),有些神采奕奕(准备放假)。
- 疲惫的 = 刚经历过"高强度学习"(类似Ki67高 = 刚分裂)
- 神采的 = 处于"蓄势待发"状态
通过表情,你能猜出谁最近经历了什么。
第二步:看"站位"猜关系(邻域分析)
观察合影里学生的站位:
- 学霸周围常围着问问题的 → 学霸促进别人学习
- 活跃分子扎堆的地方 → 互相带动气氛
- 两者混坐的区域 → 可能互相影响
关键洞察:站位反映了他们之间的相互作用规则。
第三步:画"关系图"(相图)
根据站位和表情,画出一张关系图:
plain
Copy
plain
如果学霸多 → 活跃分子被压制(太严肃,玩不起来)
如果活跃分子多 → 学霸也受影响(开始参与活动)
如果两者平衡 → 形成稳定的小团体第四步:推演时间线(数值模拟)
从开学第一天的站位(初始条件),根据关系图,推演整个学期的变化:
- 第1个月:活跃分子先抱团(快速上升)
- 第2个月:学霸开始组织学习(缓慢追赶)
- 期末:达到平衡(稳定状态)
核心类比总结
| 真实场景 | OSDR对应 | 简单理解 |
|---|---|---|
| 班级合影 | 组织活检切片 | 单一时间点的快照 |
| 学生表情 | Ki67标记 | 细胞"最近忙不忙"的标志 |
| 学生站位 | 细胞空间位置 | 谁和谁挨着,互相影响 |
| 关系规则 | 统计模型 | 不同类型细胞如何相互作用 |
| 学期动态 | 时间演化曲线 | 从开学到毕业的变化过程 |
一句话概括
OSDR就像从一张班级合影,通过观察"谁挨着谁"和"谁刚考完试很累",推断出整个学期"学霸"和"活跃分子"群体是怎么此消彼长的。
它把空间上的分布差异 (不同区域细胞密度不同)转化为时间上的动态过程(这些密度组合如何演化),实现了"从一张照片看一部电影"。
代码
https://github.com/JonathanSomer/osdr
┌─────────────────────────────────────────────────────────────┐
│ 输入:空间蛋白质组学数据(IMC等) │
│ - 细胞类型标记 │
│ - 细胞分裂标记(Ki67) │
│ - 细胞空间坐标 │
└─────────────────────────────────────────────────────────────┘
↓
┌─────────────────────────────────────────────────────────────┐
│ 步骤1:邻域特征提取 │
│ - 对每个细胞,计算半径r内各类型细胞数量 │
│ - 构建邻域组成向量 N(x) = (n₁, n₂, ..., nₖ) │
└─────────────────────────────────────────────────────────────┘
↓
┌─────────────────────────────────────────────────────────────┐
│ 步骤2:分裂概率建模(逻辑回归) │
│ - 特征:邻域细胞计数 │
│ - 目标:Ki67 > 阈值(分裂标记) │
│ - 输出:p⁺¹(N) = 分裂概率函数 │
└─────────────────────────────────────────────────────────────┘
↓
┌─────────────────────────────────────────────────────────────┐
│ 步骤3:构建动态系统 │
│ - 假设死亡概率 p⁻¹ ≈ 平均分裂率(常数) │
│ - 构建ODE:dXᵢ/dt = Xᵢ(p⁺¹(X) - p⁻¹) │
└─────────────────────────────────────────────────────────────┘
↓
┌─────────────────────────────────────────────────────────────┐
│ 步骤4:相图分析与可视化 │
│ - 在状态空间计算变化方向向量场 │
│ - 识别固定点(稳定/不稳定/半稳定) │
│ - 绘制零斜线(nullclines) │
└─────────────────────────────────────────────────────────────┘
↓
┌─────────────────────────────────────────────────────────────┐
│ 步骤5:空间随机模拟(可选) │
│ - 从初始组织状态出发 │
│ - 基于概率进行蒙特卡洛模拟(分裂/死亡/无变化) │
│ - 追踪细胞群体随时间的演化 │
└─────────────────────────────────────────────────────────────┘
参考
- Temporal tissue dynamics from a spatial snapshot
- https://github.com/JonathanSomer/osdr