真菌病原体已致数百万人类死亡,还造成全球20%作物减产,且目前临床抗真菌药类别少,与农业杀菌剂交叉使用加速了耐药菌株进化(如烟曲霉环境耐药株可感染人)。FungAMR数据库通过人工精心整理了501篇已发表研究,旨在解决真菌耐药性数据分散、质量参差不齐的问题,并为研究耐药机制、开发检测工具和新型抗真菌药物提供高质量的数据资源。

数据库链接
数据内容与规模
▶ 数据量
人工审阅501篇文献,共35,792条突变记录。
▶ 覆盖范围
**物种:**涵盖95种具有临床和农业相关性的真菌病原体;
**基因:**涉及246个基因;
**药物:**包含208种药物(其中118种为抗真菌药)。
▶ 突变类型
包括氨基酸替换、拷贝数变异(CNV)、插入/缺失等基因组变化。
核心创新与特点
▶ 突变置信评分
每条突变赋予置信度评分(1-8分),用于评估支持其导致耐药性的证据强度(1分最强,如在易感病原体中直接改造出该突变;8分最弱,如在自然分离耐药株中发现突变),这有助于用户评估数据的可靠性。
▶ 耐药机制核心发现
**耐药机制的高度趋同:**研究发现不同真菌物种在基因和突变水平上存在显著的进化趋同。例如,Cyp51基因的Y132F/H突变在超过20个物种中被发现与唑类耐药相关。
**交叉耐药性普遍:**突变通常导致同一类药物内部的交叉耐药。此外,在部分基因(如甾醇合成通路相关基因)中的突变,还会导致不同类别药物之间(如唑类与多烯类)的交叉耐药,这对临床和农业用药构成了严峻挑战。
**功能预测与结构映射:**利用GEMME和FoldX预测突变对蛋白功能和稳定性的影响;发现多数耐药突变为功能丧失型(LOF),如FCY1、FUR1、ERG3等;通过蛋白结构映射发现突变常聚集在活性位点、蛋白界面或结构核心区域。
▶ 配套的生物信息学工具
开发了一款用户友好的计算工具ChroQueTas,能够利用FungAMR的数据,快速在真菌基因组中筛查已知的AMR突变,便于基因分型检测和耐药性监测。
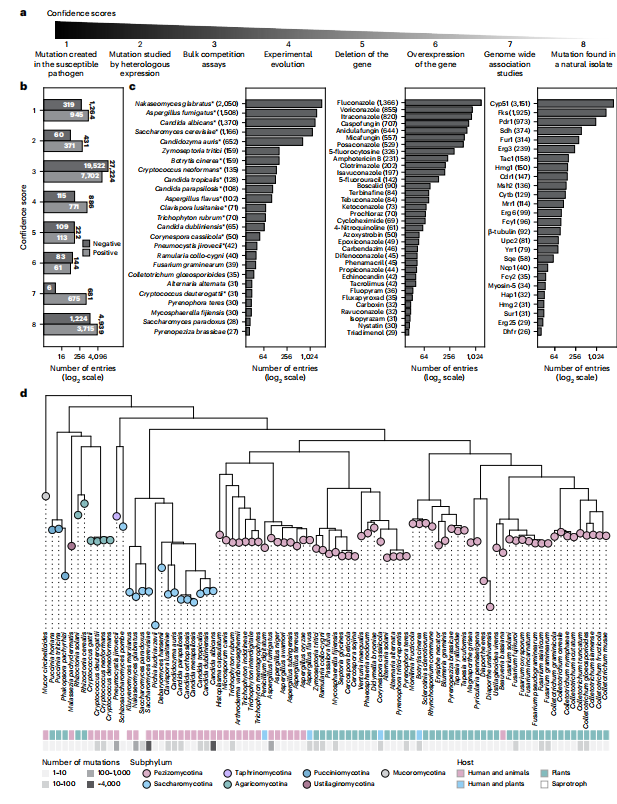
图 FungAMR数据概览:置信评分、物种、抗真菌药物及蛋白分布
FungAMR是首个经过大规模人工审阅的真菌抗真菌耐药突变综合性数据库。它揭示了真菌耐药性在分子层面的高度趋同性和交叉耐药风险,为理解耐药进化、指导抗真菌药物研发与优化、以及开发分子诊断工具提供了不可或缺的核心资源。该数据库的建立标志着在应对日益严峻的真菌耐药性威胁方面迈出了关键一步。
参考文献
FungAMR: a comprehensive database for investigating fungal mutations associated with antimicrobial resistance. Nat Microbiol. 2025 Sep;10(9):2338-2352. doi: 10.1038/s41564-025-02084-7.