拷贝数变异学习手册(Python版本)
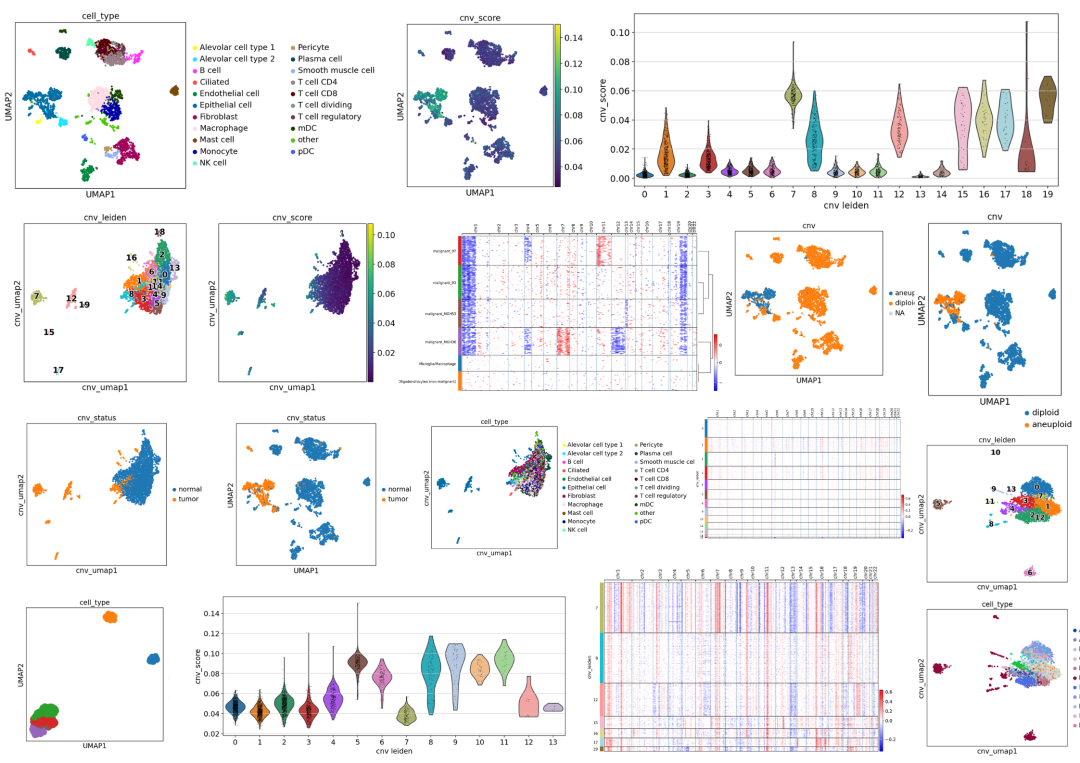
拷贝数变异(Copy number alterations,以下简称CNA) 是一种重要的基因组变异,在癌症的发生和发展过程中起着至关重要的作用。确定肿瘤细胞中CNA的特征对早期肿瘤检测、划分肿瘤异质性、了解肿瘤进展模式和揭示耐药机制具有重要意义。随着单细胞RNA测序(scRNA-seq)的蓬勃发展,研究人员开发出了多种计算方法来从scRNA-seq研究中推断CNA。目前从scRNA-seq数据中推断CNA的计算方法大致可分为两类。一类是基于表达的,即直接从基因表达推断CNA。这类工具包括inferCNV、copykat和SCEVAN。这些工具的工作原理是,CN扩增(AMPs)或缺失(DELs)将分别导致受影响基因组区域内基因的上调或下调。InferCNV 利用基因窗口的校正移动平均数;copykat 采用综合贝叶斯分割方法;SCEVAN采用多通道分割算法。第二类将基因表达与等位基因信息相结合,相关工具有Numbat和CaSpER等。
往期我们 也基于R版本验证了其中部分软件的功能,感兴趣的小伙伴可以 点击**R语言scRNA-seq拷贝数变异分析** 学习哦~
学习手册部分图片集锦:
优惠订阅资料 或参与课程 请联系**Biomamba_zhushou**
更多生信教程可见: 为什么我们敢开放终身订阅
-Biomamba
所见即所得
以html格式提供学习手册,可在浏览器中打开并翻阅学习:

教程目录:
零、欢迎关注
一、前言
1.1 研究背景
1.2 主要结果
1.3 小结
二、准备工作
2.1 环境准备
2.2 库准备
三、infercnvpy
3.1 数据下载
3.2 参数详解
3.3 运行infercnvpy
3.4 计算每个细胞的cnv分数
3.5 可视化
四、通过CNV谱进行聚类并识别肿瘤细胞
4.1 cnv聚类分群
4.2 cnv展示umap
4.3 scanpy展示cnv结果
4.4 肿瘤细胞分类
4.5 肿瘤和正常细胞分开绘制热图
五、内嵌copykat
5.1 数据读入
5.2 参数详解
5.3 运行copycat
5.4 计算每个细胞的cnv分数
5.5 可视化
5.6 通过cnv谱进行聚类并识别肿瘤细胞
5.7 肿瘤和正常细胞分开绘制热图
六、对比R版本的infercnv
七、如何获取基因在染色体上的位置
八、软件版本
九、单细胞教程全收录
十、欢迎致谢
文末下载链接中包含以下内容:

测试文件,总大小10.62GB
往期推送
Biomamba 生信基地现已开放终身订阅,现已包含几十篇订阅资料,未来37年持续更新:为什么我们敢开放终身订阅
2025年我们零差评完成订阅任务(2026订阅须知),2026已更新订阅内容:
风靡一时的scTenifoldKnk单细胞虚拟基因敲除,准不准?
scRNA拟时序分析三大Python包: palantir、PAGA、RNAvelocity
正刊都在用的AI驱动蛋白质从头设计流程:RFdiffusion+ProteinMPNN+AlphaFold3
转录因子、基因共表达网络分析手册:pySCENIC在脑、黑色素瘤中的应用
解锁前需阅读:2026订阅须知