亮点
・MicrobeAtlas包含240万份经统一分析的微生物群落样本
・可通过功能丰富的网站在全球范围内追踪微生物类群及群落
・详尽的生态系统注释及元数据支持各类研究问题的开展
・全球范围分析揭示了普遍存在的分类学、生物地理及泛化性趋势
摘要
环境DNA测序彻底改变了对微生物多样性和生态学的认知。如今,微生物组测序已覆盖全球各个角落------从深层地下到山顶,涵盖众多宿主、生物群系和环境条件。然而,测序与分析策略的多样性阻碍了普适性洞见的获取。MicrobeAtlas将超过200万份微生物组样本整合为单一资源,通过标准化处理助力跨技术研究发现。该数据库以可调节的小亚基核糖体RNA(SSU rRNA)标记基因分辨率对群落进行层级化定量,并提供包含丰富地理信息的详细元数据。与基因组、表型和生态资源的关联支持多模态研究。微生物谱系可在不同环境中被可靠追踪,包括大量罕见、未表征的物种。研究揭示了重复出现的群落结构和地理偏好,以及全球范围内特定分类群的泛化性趋势。借助MicrobeAtlas,已知和新描述的物种及群落均可轻松纳入其生态背景中,充分利用以往研究成果。
#微生物生态系统 #微生物组数据库 #生物地理学 #操作分类单元OTU #环境DNA #微生物多样性 #泛化性与特化性
结果
MicrobeAtlas数据集生成与分析流程
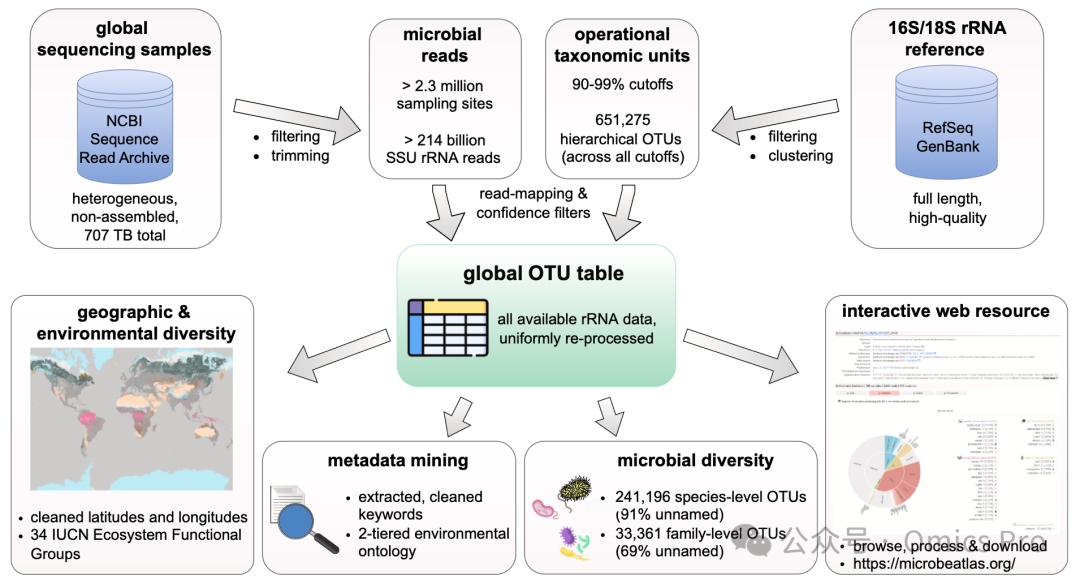
图 1 MicrobeAtlas数据获取与分析流程
靶向和非靶向微生物测序的原始数据从NCBI序列读取档案库(SRA)下载、清洗,并与按灵活阈值(如种水平:98%,科水平:90%)预聚类的OTU进行比对。最终生成的OTU表与地理信息、共识分类学、群落簇信息以及详细的本体论和基于关键词的元数据相关联。交互式网络应用程序支持对整个群落和单个类群的深入探索性分析与下载。
全球微生物组结构图谱
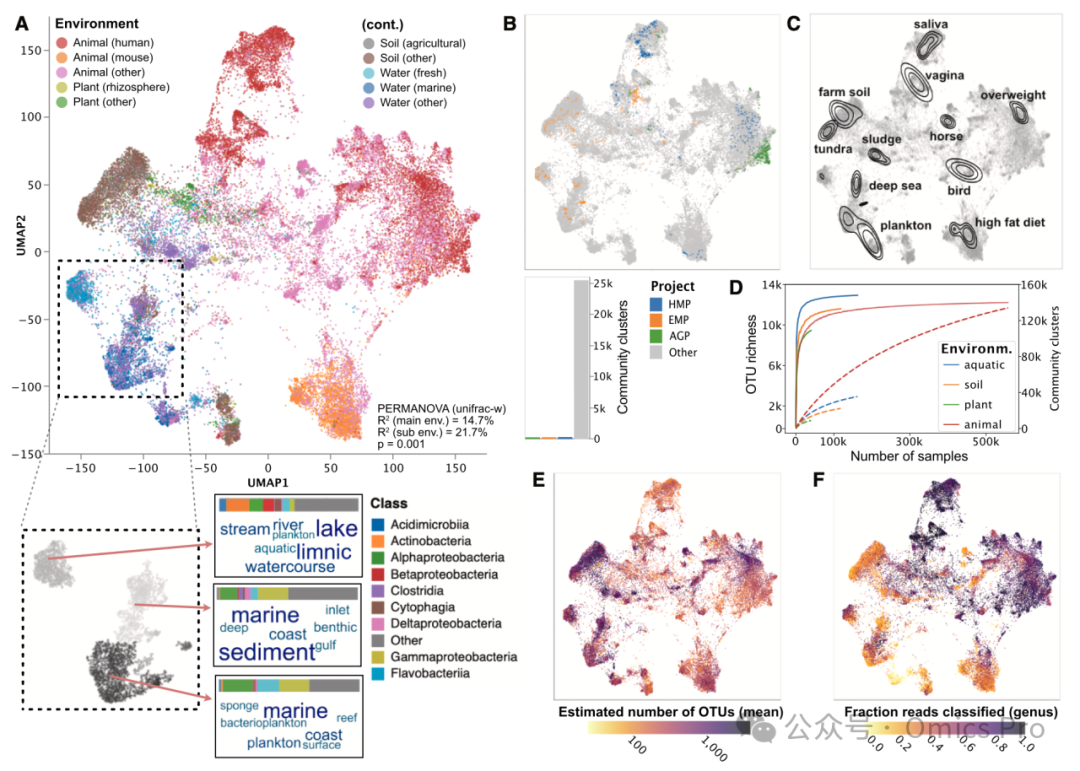
图 2 基于1,153,349份筛选测序样本生成的26,487个稳健群落簇的UMAP投影
(A) 上图:基于布雷-柯蒂斯相异度的群落簇(圆点),按共识主环境和子环境着色(「其他」包含无亚环境注释的簇)。移除无明确主环境的簇。下图:灰度颜色表示基于均匀流形近似与投影UMAP坐标(欧氏距离)计算的基于噪声的空间聚类应用DBSCAN密度簇。分类水平柱状图表示每个分类水平和DBSCAN簇的平均相对丰度(按簇归一化)。词云显示每个DBSCAN簇中7个最普遍的关键词,文本大小和深浅度与关键词频率相关。扩展「其他」类别后,对所有子环境进行置换多元方差分析PERMANOVA。
(B) 上图:按主要测序项目(人类微生物组计划HMP、地球微生物组计划EMP、美国肠道计划AGP)或其他研究着色的群落簇。下图:各项目类型的群落簇数量。
(C) 示例关键词在群落簇中频率的核密度估计(按关键词归一化)。
(D) 按样本环境分层,群落簇总数(虚线)或OTU数(实线;97% OTU水平)随采样量的变化。
(E、F) 按估计OTU丰富度(E;97% OTU水平)或属水平分类读数比例(F)着色的群落簇。
未表征微生物多数派的生态洞见
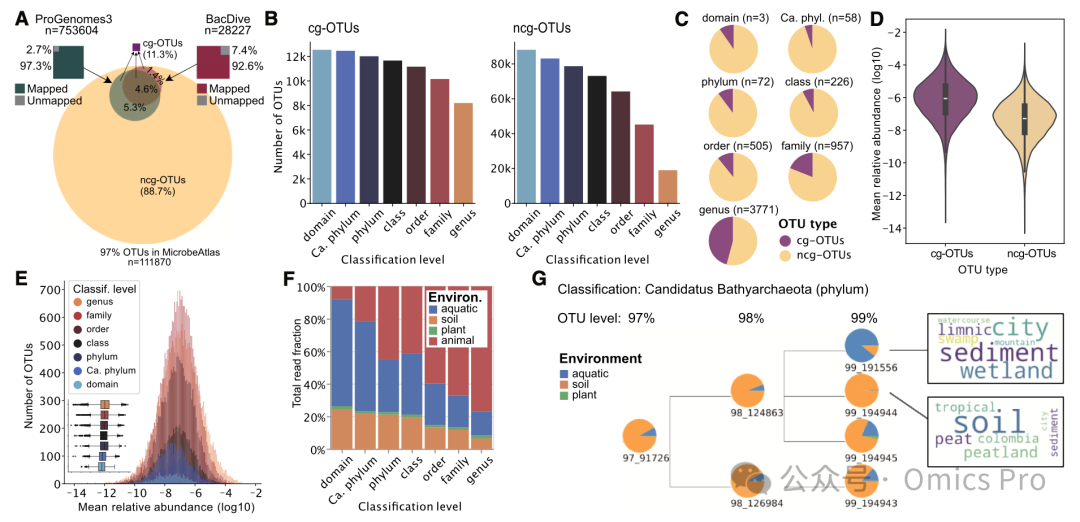
图 3 MicrobeAtlas OTU的分类学表征与生态学特征
(A) 圆圈表示映射到proGenomes3或BacDive序列(最佳匹配相似度>97%)或未映射的MicrobeAtlas OTU。映射的OTU统称为「培养/基因组OTU(cg-OTUs)」,未映射的OTU称为「非cg-OTUs(ncg-OTUs)」。方块表示映射到MicrobeAtlas OTU的proGenomes3(绿色)和BacDive(红色)序列比例,灰色表示未映射序列。
(B) 有无培养菌株或基因组注释的OTU在不同分类等级的可分类数量(蓝色表示分类等级较低,红色表示分类等级较高)。
(C) 每个分类等级中至少有1个带注释培养菌株或基因组的类群比例(紫色)。
(D) 有无培养菌株或基因组注释的物种平均相对丰度(对数10尺度)(内框为4分位距;须为1.5×四分位距;密度为高斯核估计)。
(E) 不同分类等级可分类OTU的丰度分布(蓝色表示表征程度较低)。插图:相同丰度的箱线图(箱为4分位距;须为1.5×四分位距)。
(F) 不同分类等级OTU的环境分布(映射读数比例,按等级归一化;去除真核生物)。
(G) 1个未表征97%-OTU及其子OTU的环境分布(平均相对丰度,重新缩放)。词云显示2个OTU在所有栖息样本中7个最普遍的关键词,按相对丰度加权。文本大小根据丰度加权关键词频率调整。
跨大陆与生物群系的生物地理趋势
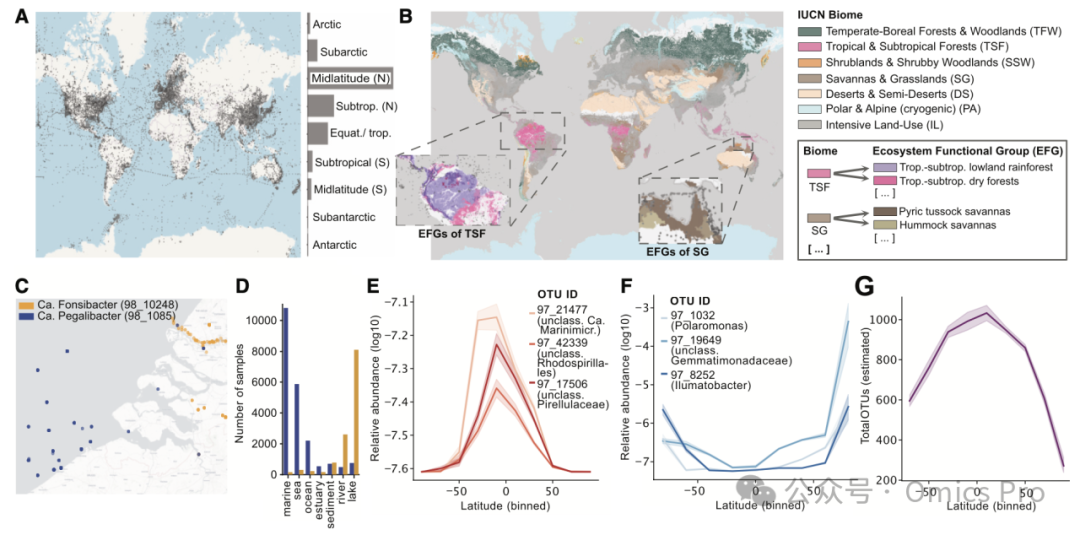
图 4 微生物类群和群落的生物地理模式
(A) 不同气候带微生物测序样本的全球分布。
(B) 世界自然保护联盟IUCN生物群系和生态功能群EFG地图,将微生物群落与宏观生态特征关联。全球地图按生物群系着色,放大区域按生态功能群着色(灰色圆点为MicrobeAtlas样本)。
(C) 2个海洋浮霉菌目OTU的生态位分离示例(圆点为观测分布,显示全球分布的局部示例)。
(D) (C) 中每个OTU在各子环境的全球样本数量。
(E、F) 偏好热带和亚热带地区(E)或极地和亚极地地区(F)的示例OTU。线和误差带表示10个等大小纬度区间内对数转换相对丰度的平均值和95%置信区间(1,000次自举)。每个OTU的分布仅限于其主环境(按最高相对丰度定义)。
(G) 海洋群落OTU丰富度随纬度的变化。线、误差带和区间定义同(E)和(F)。
跨环境与分类群的生态泛化性模式
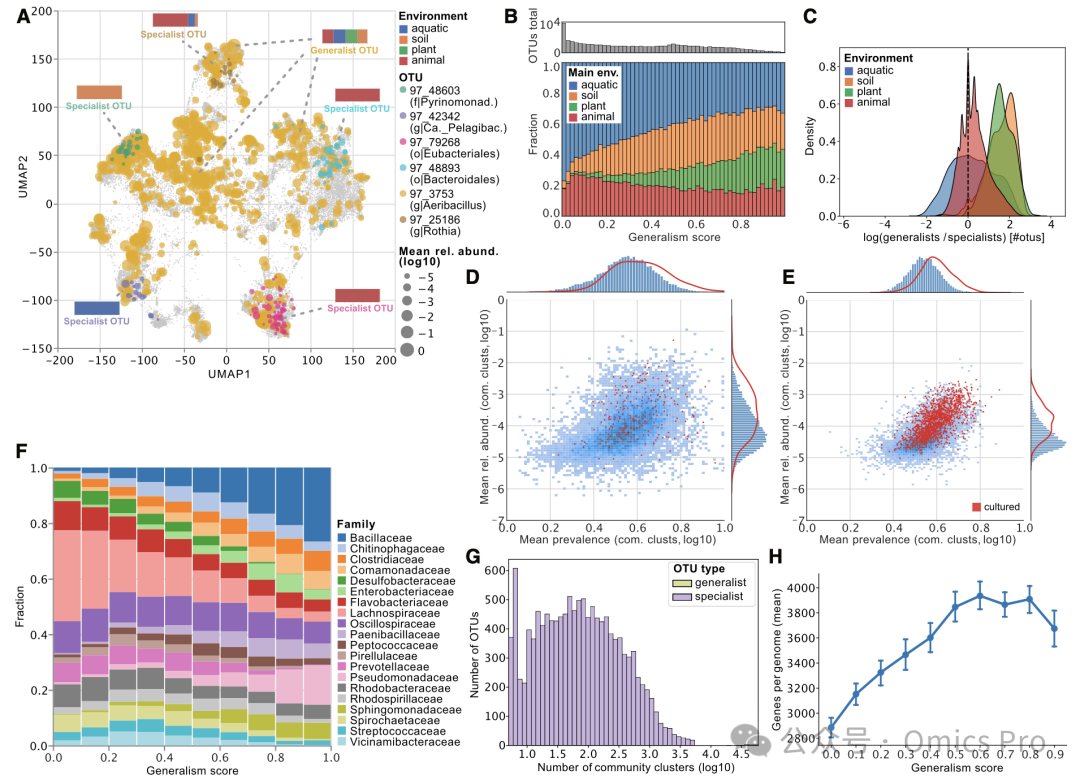
图 5 跨环境与分类群的栖息地泛化性与特化性趋势
(A) 1个泛化型OTU(黄色圆点)和5个特化型OTU(其他颜色;灰色表示无显示OTU存在)的UMAP群落簇丰度分布。柱状图表示每个OTU的环境相对丰度分布。
(B) 上图:每个归一化泛化性得分区间的OTU数量。下图:按主环境(按最高相对丰度定义)分层的每个泛化性得分区间的OTU比例。
(C) 按环境分组的每个样本中前10%泛化种与前10%特化种数量的对数比。
(D、E) 前10%特化种(D)和前10%泛化种(E)在群落簇中的平均流行度与相对丰度(去除0值)的关系。红点表示有培养代表的OTU。培养代表的边缘密度为高斯核估计。
(F) 20个最常见分类科的比例,按归一化泛化性得分分组。仅显示映射到这些科的OTU。
(G) 前10%泛化型(绿色)和前10%特化型(紫色)OTU的群落簇数量密度(对数10尺度)。
(H) 每个泛化性得分区间内可映射到proGenomes3的OTU的平均基因数量。线和误差带表示平均值和95%置信区间(1,000次自举)。
数据与代码
现有公开数据
主要处理后的数据
下游分析的原始代码
www.github.com/meringlab/MicrobeAtlas_companion
Zenodo
https://doi.org/10.5281/zenodo.18314332
详细总结
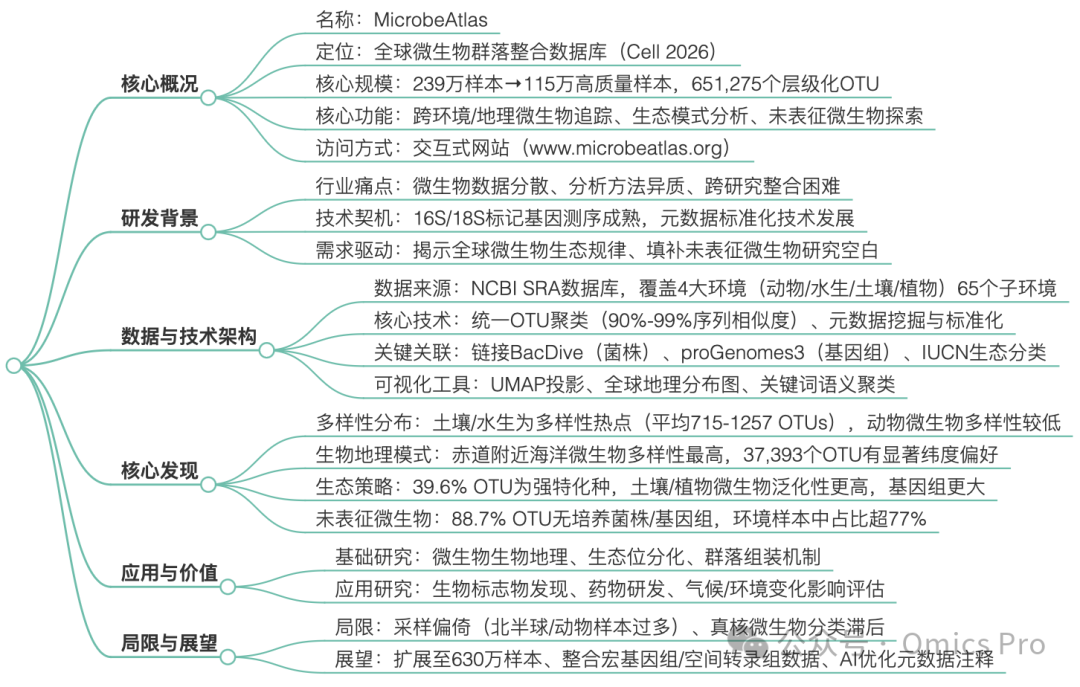
思维导图
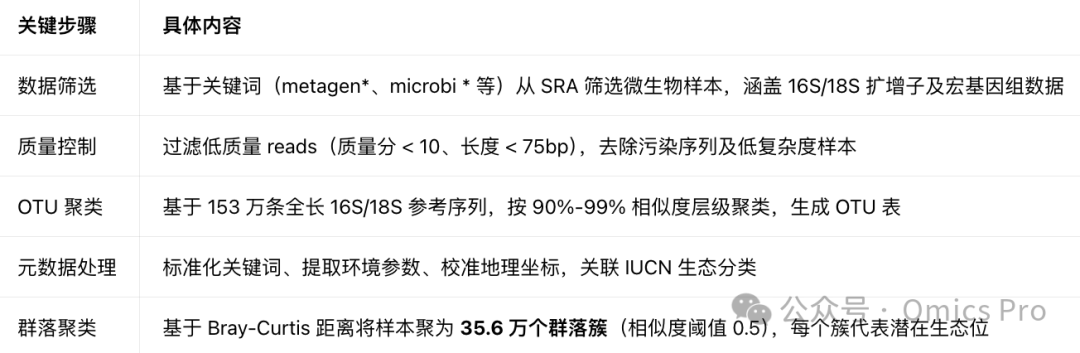
技术架构与分析流程
参考
Cell. 2026 Apr 2;189(7):2092-2107.e17. doi: 10.1016/j.cell.2026.01.021.
The MicrobeAtlas database: Global trends and insights into Earth's microbial ecosystems
注:AI辅助创作,如有错误欢迎指出。内容仅供参考,不构成任何建议。